Luigi Ricciardi 1 , Rosa Mazzeo 2,*© , Angelo Raffaele Marcotrigiano 1 , Guglielmo Rainaldi 3 , Paolo Iovieno 4 , Vito Zonno 1 , Stefano Pawan 1© jeung Concetta Lotti 2,*
- 1 Departemen Taneuh, Tutuwuhan sarta Élmu Pangan, Genetika tutuwuhan jeung beternak Unit Universitas Bari, Via Amendola 165 / A, 70125 Bari, Italia; luigi.ricciardi@uniba.it (LR);angelo.marcotrigiano@uniba.it (ARM); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 Jurusan Élmu Pertanian, Pangan sareng Lingkungan, Universitas Foggia, Liwat Napoli 25, 71122 Foggia, Italia
- 3 Departemen Biosciences, Biotéhnologi jeung Biopharmaceuticals, Universitas Bari, Via Orabona 4, 70125 Bari, Italia; guglielmo.rainaldi@uniba.it
- 4 Departemen Téhnologi Énergi, Bioenergy, Biorefinery sarta Divisi Héjo Kimia, ENEA Trisaia Panalungtikan Center, SS 106 Ionica, km 419+500, 75026 Rotondella (MT), Italia; paolo.iovieno@enea.it
* Susuratan: rosa.mazzeo@unifg.it (RM); concetta.lotti@uifg.it (CL)
abstrak:
Bawang (Allium cepa L.) nyaéta pepelakan sayur kadua anu paling penting di dunya sareng diapresiasi sacara lega pikeun kauntungan kaséhatanna. Sanajan pentingna ékonomis signifikan sarta nilaina salaku dahareun fungsional, bawang geus kirang ditalungtik ngeunaan karagaman genetik na. Di dieu, urang surveyed variasi genetik dina "Acquaviva bawang beureum" (ARO), a landrace kalawan sajarah abad-lami budidaya di hiji kota leutik di propinsi Bari (Apulia, Southern Italia). Sakumpulan 11 spidol mikrosatelit digunakeun pikeun ngajalajah variasi genetik dina kumpulan plasma nutfah anu diwangun ku 13 populasi ARO sareng tilu jinis komérsial umum. Analisis struktur genetik sareng metode parametrik sareng non-parametrik nunjukkeun yén ARO ngagambarkeun kolam renang gen anu jelas, jelas béda ti Tropea sareng Montoro landraces anu sering kaliru. Dina raraga nyadiakeun pedaran bulbs, biasana dipaké pikeun konsumsi seger, eusi padet larut tur pungency dievaluasi, némbongkeun rasa amis luhur dina ARO nu aya kaitannana ka dua landraces disebutkeun di luhur. Gemblengna, ulikan ayeuna mangpaat pikeun valorization hareup ARO, nu bisa diwanohkeun ngaliwatan labél kualitas nu bisa nyumbang kana ngawatesan frauds komérsial sarta ngaronjatkeun panghasilan tina smallholders.
perkenalan
Genus Allium ngawengku kira-kira 750 spésiés [1], diantarana bawang bombay (Allium cepa L., 2n = 2x =16) mangrupa salah sahiji anu pang nyebarna. A. cepa boga siklus biennial sarta outcrossing kabiasaan réproduktif. Kiwari, produksi bawang bombay global (97.9 Mt) ngajadikeun eta pepelakan sayur pangpentingna kadua sanggeus tomat [2]. Saprak jaman baheula, bulbs bawang geus dipaké duanana salaku dahareun jeung dina aplikasi ubar rahayat. Mémang, urang Mesir kuno parantos ngalaporkeun sababaraha rumus terapi dumasar kana panggunaan bawang bodas sareng bawang bombay dina lontar médis 1550 SM, Codex Ebers [3].
Sayuran anu serbaguna sareng séhat ieu dikonsumsi atah, seger, atanapi salaku produk olahan, sareng dianggo pikeun ningkatkeun rasa seueur masakan. Sababaraha studi panganyarna ngaku yen konsumsi bawang bisa ngurangan résiko panyakit cardiovascular [4,5], obesitas [6], diabetes [7], sarta sagala rupa wangun kanker [8-10]. Proprieties kaséhatan bawang mindeng attributed ka tingkat luhur dua kelas sanyawa nutraceutical: flavonoid jeung alk(en)yl cysteine sulphoxides (ACSOs). Kelas munggaran kalebet flavonol sareng anthocyanin. Quercetin mangrupikeun flavonol utama anu tiasa didéteksi, dipikanyaho ku antioksidan anu kuat sareng sipat anti-radang dina pamulung radikal bébas sareng ngabeungkeut ion logam transisi. [11]; sedengkeun anthocyanin masihan warna beureum/ungu pikeun sababaraha variétas bawang. Sedengkeun pikeun ACSOs, anu paling loba pisan nyaéta isoalliin [(+)-trans-S-1-propenyl-L-cysteine sulfoxide] [12], asam amino sulfur non-volatile sareng non-protéinogenik anu disimpen dina sél, anu sacara henteu langsung tanggung jawab pikeun aroma sareng rasa anu pikaresepeun tina bawang. [13]. Kana gangguan jaringan, isoalliin dibeulah ku énzim alliinase pikeun ngahasilkeun runtuyan sanyawa volatil (piruvat, amonia, thiosulphonate jeung propanethial S-oksida) nu ngakibatkeun tearing sarta ngabalukarkeun bau pikaresepeun (pungency). [14]. The pungency bawang mindeng diukur salaku jumlah, per gram beurat seger, asam piruvat dihasilkeun ku hidrolisis. [15.16].
Di nagara Citarum Tengah, diusulkeun salaku salah sahiji puseur diversity sekundér tina A. cepa [17.18], bulbs bawang nembongkeun variability lega dina bentuk, ukuran, warna, bahan garing, sarta pungency [19-hiji]. Sumawona, pupuk dumasar walirang, prakték agronomis, jinis taneuh, kaayaan iklim, sareng genotip kultivar atanapi landraces tiasa mangaruhan kualitas bohlam ku cara masihan nilai organoleptik sareng nutrisi anu unik. [23-hiji]. Di Italia, sanajan kasadiaan germplasm bawang bombay lega, ngan sababaraha variétas bawang bombay mindeng subjected kana studi ilmiah sarta dicirikeun leres. [28.29].
Karakterisasi genetik sareng fenotip agro-biodiversitas penting pisan pikeun mastikeun konservasi sumber daya genetik pepelakan sareng ngamajukeun panggunaan genotip khusus dina ranté nilai. [30-hiji]. spidol runtuyan basajan (SSR) geus mindeng dipilih pikeun pemetaan [33-hiji], sidik DNA jeung diskriminasi kultivar [36-hiji], sarta estimasi dipercaya tina variabilitas genetik di jero jeung di antara landraces [39-hiji], Kusabab aranjeunna locus spésifik, multi-allélik, diwariskeun sacara kodominasi, kacida reproducible, sarta cocog pikeun genotyping otomatis.
Dina ulikan ayeuna, urang museurkeun perhatian urang kana hiji landrace tradisional Apulian, anu "Acquaviva bawang beureum" (ARO), nu dibudidayakan nurutkeun métode pertanian organik di wewengkon leutik kota Acquaviva delle Fonti, di propinsi Bari. (Apulia, Italia Kidul). The bulbs of landrace ieu badag sarta flattened sarta warna beureum sarta lolobana dipaké dina resep lokal. Sanaos ARO nampi tanda kualitas "Slow Food Presidium", produksina tiasa dipromosikeun sareng ditangtayungan ku tanda kualitas Uni Éropa sapertos indikasi geografis (PGI) sareng sebutan asal anu ditangtayungan (POD), sabab ieu tiasa nyumbang kana ngawatesan frauds komérsial sarta ngaronjatkeun panghasilan tina smallholders. Di dieu, spidol molekular SSR dianggo salaku alat anu kuat pikeun meunteun variasi genetik diantara populasi ARO sareng ngabedakeun landrace ieu tina dua landraces bawang beureum Italia Kidul. Salajengna, kami diperkirakeun pungency sareng eusi padet larut pikeun ngevaluasi rasa ARO dina hubunganana sareng paménta pasar.
Results
Ngadegkeun Acquaviva Bawang Beureum Kumpulan Nutfah jeung Karakterisasi Morfologis
Bibit 13 populasi landrace ARO, disumbangkeun ku patani dina kerangka proyék BiodiverSO Apulia Region dipaké pikeun nyieun kumpulan germplasm ARO.
Deskriptor morfologis, patali jeung bohlam, kulit, jeung daging dikumpulkeun dina plasma nutfah ARO jeung dina tilu landraces bawang, dua milik landrace "Tropea bawang beureum" (TRO) jeung hiji landrace "Montoro tambaga bawang" (MCO) (Gambar. 1). Kabéh bulbs ARO éta datar tur dicirikeun ku kulit éksternal beureum jeung daging jeung nuansa béda tina beureum. Sabalikna, daging bohlam TRO pinuh beureum, sedengkeun daging bohlam MCO kurang pigmén (Tabel S1). Analisis biokimiawi diidinan ngira-ngira eusi larut padet sareng pungency. Salaku dilaporkeun dina Table 1, nilai rata-rata eusi larut padet bulbs dina populasi ARO éta 7.60, sarta ranged ti 6.00 (ARO12) ka 9.50 ° Brix (ARO11 na ARO13). Nilai ieu langkung luhur tibatan anu diperkirakeun pikeun landraces TRO sareng MCO (masing-masing 4.25 sareng 6.00 ° Brix).

Méja 1. Eusi Leyur Padet tur Nilai Pungency Ditaksir dina "Acquaviva Bawang Beureum" (ARO), "Tropea Beureum Bawang" (TRO), sarta "Montoro Tambaga Bawang" (MCO) Populasi *.
| kode | Kandungan Padet Leyur (Brix) | Pungency (pmolg-1 FW) | ||
| maksudna | CV y (%) | maksudna | CV y (%) | |
| ARO1 | 6.25 D * | 5.65 | 5.84 ab * | 23.78 |
| ARO2 | 7.25 DC | 4.87 | 6.51 ka | 22.98 |
| ARO3 | 7.50 BCD | 9.42 | 5.28 ab | 22.88 |
| ARO4 | 7.50 BCD | 0.00 | 6.97 ka | 3.74 |
| ARO 5 | 7.50 BCD | 0.00 | 6.80 ka | 9.68 |
| ARO6 | 6.25 D | 5.65 | 4.51 ab | 39.18 |
| ARO7 | 7.25 DC | 4.87 | 5.25 ab | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 ka | 3.49 |
| ARO9 | 8.25 ABC | 4.28 | 6.84 ka | 0.15 |
| ARO10 | 7.00 DC | 0.00 | 5.94 ab | 6.57 |
| ARO11 | 9.50 A | 7.44 | 5.54 ab | 16.43 |
| ARO12 | 6.00 D | 0.00 | 4.91 ab | 9.70 |
| ARO13 | 9.50 A | 7.44 | 6.63 ka | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18 ab | 2.66 |
| TRO1 | 4.25 E | 8.31 | 2.80 b | 2.10 |
| TRO2 | 4.25 E | 8.31 | 4.28 ab | 4.79 |
* Hartina jeung hurup sarua dina hurup gede atawa leutik henteu statistik béda dina 0.01P atawa 0.05P, masing-masing (SNK urang Test). y Koéfisién variasi.
Nilai rata-rata pungency ARO, ditaksir ku cara eusi asam piruvat, éta 6.00, ranged ti 4.51 pmol g-1 FW (ARO6) ka 7.04 (ARO8). Nilai ieu langkung luhur tibatan anu diperkirakeun dina TRO sareng MCO landraces (3.54 pmol g-1 FW sareng 4.18 pmol g-1 FW, masing-masing).
SSR Polymorphism sarta Hubungan genetik diantara Accessions
Dina ulikan ayeuna, 11 tina 37 kombinasi primer SSR anu diuji nyayogikeun polimorfisme lokus tunggal, nyaéta, ngahasilkeun paling seueur dua produk amplifikasi dina hiji individu. Gemblengna, 55 alél dideteksi dina 320 individu kalayan sajumlah alél per lokus mimitian ti 2 (ACM147 sareng ACM 504) dugi ka 11 (ACM132) sareng nilai rata-rata 5 alél (Table). 2). Dina populasi individu, jumlah alél (Na) dibasajankeun 1.94 (ACM147 sareng ACM504) dugi ka 5.38 (ACM132), sedengkeun jumlah efektif alél (Ne) dibasajankeun 1.41 (ACM152) dugi ka 2.82 (ACM449). Kasalahan antara nilai Na jeung Ne éta alatan ayana alél kalawan frékuénsi low dina populasi sarta dominasi ukur sababaraha alél. Nilai heterozygosity (Ho) anu dititénan pangluhurna disorot pikeun ACM138 sareng ACM449 (0.62), sedengkeun anu panghandapna pakait sareng ACM152 (0.25). Diperkirakeun heterozygosity (Anjeunna), nu pakait jeung ekspektasi teoritis dina populasi panmictic, ranged ti 0.37 (ACM504) ka 0.61 (ACM132, ACM138, sarta ACM449). Indéks fiksasi Wright urang (Fis), ditampilkeun nilai deukeut enol (rata-rata 0.05) pikeun sakabéh spidol, nunjukkeun nilai nu sarupa antara tingkat heterozygosity observasi jeung ekspektasi, saperti nu diharapkeun pikeun spésiés outcrossing. Efisiensi spidol SSR individu dina sidik genetik diperkirakeun ku indéks polymorphic information content (PIC), kalayan nilai rata-rata 0.48 sareng dibasajankeun 0.33 (ACM504) dugi ka 0.67 (ACM132). Indéks efisiensi anu sanés, Indéks Émbaran Shannon (I) nunjukkeun nilai rata-rata 0.84, sareng asumsi nilaina dibasajankeun 0.45 (ACM152) dugi ka 1.20 (ACM132).
Méja 2. Fitur Polimorfisme tina 11 Spidol SSR Dipaké pikeun Estimasi Karagaman Genetik dina Populasi ARO, TRO, jeung MCO. Jumlah Jumlah Alél (Na), Rentang Ukuran Pita, sareng Indéks Eusi Émbaran Polimorfik (PIC) Ngarujuk kana Jumlah Susunan 320 Individu anu Digenotip dina Ulikan ieu. Jumlah Alél (Na), Jumlah Alél Efektif (Ne), Heterozigositas Teramati (Ho), Heterozigositas Diduga (He), Indéks Fiksasi (Fis), sareng Indéks Émbaran Shannon (I) ngarujuk kana Nilai Rata-rata Diitung tina 16 Populasi, Tiap Disusun ku 20 Individu.
| Lokus. | Jumlah Na | Rentang ukuran (bp) | pic | maksudna | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| maksudna | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
Di antara populasi, ARO3, ARO6, ARO8, ARO10, TRO1, sareng MCO nunjukkeun tingkat variasi genetik anu luhur (Ho > 0.5), sedengkeun karagaman panghandapna dititénan dina populasi ARO7 (Ho = 0.27) (Tabel Tambahan S2). Gemblengna, sadaya aksési ditampilkeun Fis nilai deukeut nol (Fis nilai rata-rata = 0.054), saperti nu diharapkeun dina kaayaan kawin acak.
Analisis Varians Molekul jeung Struktur Genetik
Pembagian hirarki variasi genetik diantara sareng dina populasi diitung ku AMOVA. Hasilna nunjukkeun fraksi anu ageung tina variasi genetik dina populasi (87%). Variasi diantara populasi, 13%, kacida signifikan (P <0.001) (Tabel 3). Nilai pairwise tina parameter Fpt, analog tina indéks fiksasi Fst Wright, mimitian ti 0.002 (ARO2/ARO10) nepi ka 0.468 (ARO7/TRO2), éta signifikan (P <0.05), iwal salapan babandingan pasangan (Tabel Tambahan S3).
Méja 3. Analisis Varians Molekul 320 Genotip tina 16 Populasi allium cepa L.
| sumber | df | Jumlah Kotak | Estimasi Varians | Varians (%) | Fpt | P |
| Di antara populasi | 15 | 458.63 | 1.16 | 13% | ||
| Dina populasi | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| total | 319 | 2731.62 | 8.66 |
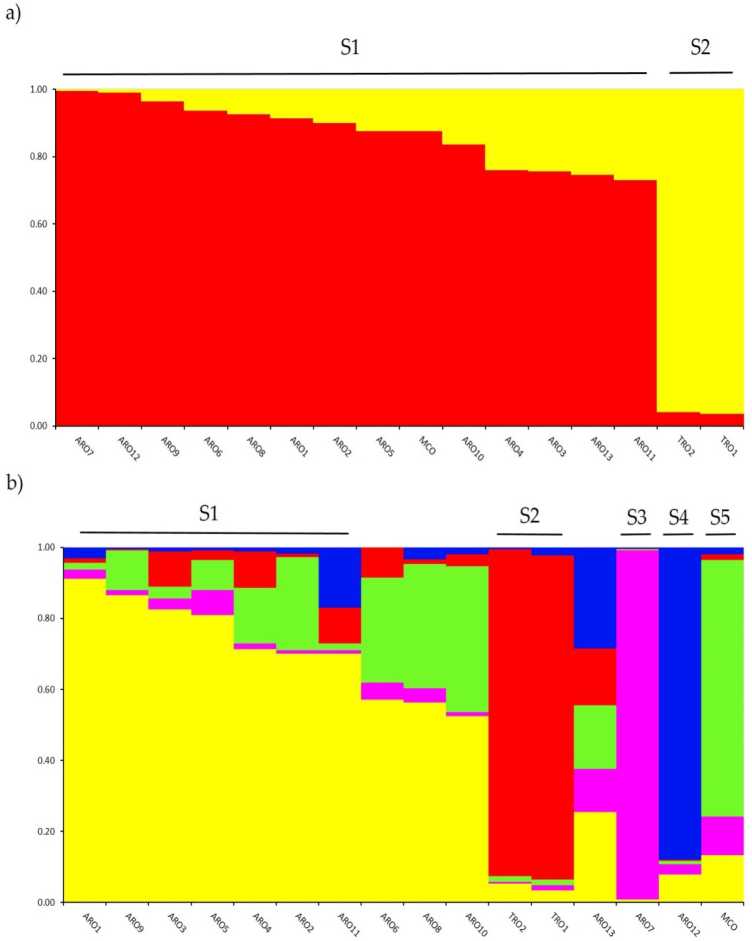
Panalungtikan ngeunaan struktur genetik dina A. cepa kempelan genotyped dina ulikan ieu dilakukeun ku cara analisis clustering basis modél admixture dilaksanakeun dina STRUKTUR software. Métode Evanno AK nyarankeun ngabagi dua klaster (K = 2) salaku anu paling informatif pikeun urang. susunan data,jeung the Teras pe pangluhurnaak ku K = 5 (Supplementaiv Rgure S1). A pikeun K = 2, ahpopulekan wenya buritigned nuju onjeungf dua klaster jeung a koefisien rnernbertoip (q) > 0.7. Salaku shown di angka 2a, klaster kahiji (ngaranna S1) kaasup MCO jeung sakabeh populasi ARO, sedengkeun klaster S2 dikelompokeun dua populasi TRO. Dina K = 5, nyadiakeun déskripsi deeper tina dataset (Gambar 2b), 75% tina aksés ditugaskeun ka salah sahiji tina lima klaster. Separation antara ARO (S1) jeung TRO (S2) dikonfirmasi, sanajan sababaraha populasi ARO ieu admixed (q <0.7) atawa dikelompokkeun misah dina dua klaster anyar S3 na S4 (ARO7 na ARO12, mungguh). Narikna, tipe komérsial MCO ngawangun klaster béda (S5) dipisahkeun tina bawang beureum Apulian.
Hubungan genetik diantara Populasi
Polimorfisme SSR diwenangkeun ngagambar dendrogram karagaman genetik sareng hasil analisis filogenetik dipidangkeun dina Gambar. 3a. Di dieu, kumpulan germplasm dibagi kana lima kelompok anu dirojong ku nilai bootstrap. Populasi ARO7 sareng ARO12 langsung dipisahkeun tina populasi sésana sareng ngawangun dua klaster anu béda. Klaster katilu kaasup dua populasi komérsial TRO, sedengkeun titik kaopat dibagi MCO tina sabelas populasi ARO. Hubungan genetik anu lumangsung diantara populasi ditalungtik deui ku cara analisis koordinat pokok (PCoA) (Gambar 3b). Salaku disorot saméméhna, populasi ARO dikelompokeun pageuh, iwal ARO12 na ARO7, nu mucunghul dina posisi terasing dina plot PCoA. Dua TRO sareng populasi MCO sumebar di panel katuhu handap plot.
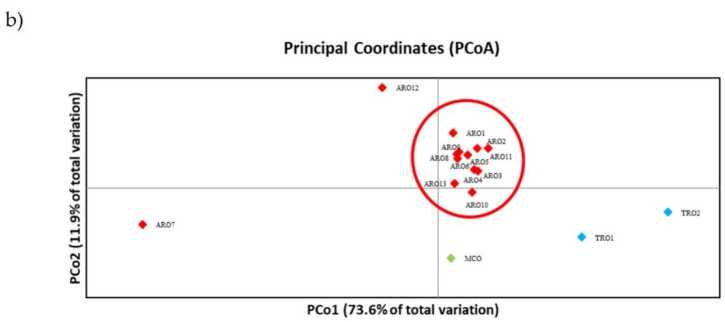
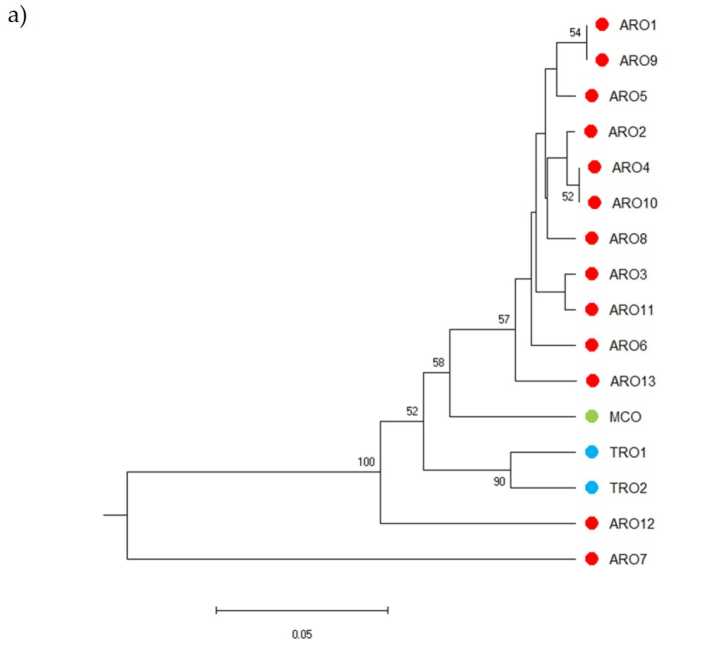
Gambar 3. Keragaman genetik diantara 16 A. cepa populasi dicirikeun dina ulikan ieu, dumasar kana profil SSR maranéhanana. (a) UPGMA dendrogram jarak genetik. Nilai rojongan Bootstrap> 50 dituduhkeun di luhur titik pakait; (b) analisis komponén poko (PCoA). Kluster dikurilingan beureum sapinuhna cocog sareng grup anu dihasilkeun ku analisis filogenetik sareng diwangun ku 11 aksési ARO.
diskusi
Dina jumlah badag agro-biodiversity tradisional dibudidayakan di Italia Kidul, landraces bawang ngagambarkeun produk Ecological nu kudu dilestarikan tina resiko erosi genetik jeung anceman ngagantian ku kultivar modern. Dina kerangka proyék régional BiodiverSO, aimed dina ngumpulkeun, characterizing, promosi, jeung safeguarding sumberdaya genetik wewengkon Apulia kuat numbu ka warisan lokal, urang ngadegkeun kumpulan bibit 13 populasi ARO landrace. Kami ngalaporkeun penilaian mimiti variasi ARO dina hal polimorfisme DNA sareng dua parameter biokimiawi, eusi asam padet sareng piruvat larut, anu aya hubunganana sareng sifat rasa sareng pentingna pikeun nampi produk anu henteu asak seger. Salaku tambahan, data dina landrace ARO dibandingkeun sareng anu dikumpulkeun dina dua landraces bawang bombay pigmented anu sering kaliru.
Analisis biokimiawi nyorot rasa amis tina 13 populasi ARO, aya hubunganana sareng eusi padet larut anu luhur sareng pungency sedeng, dumasar kana pedoman industri bawang amis. [31]. Bulbs ARO éta leuwih amis ti maranéhanana TRO na MCO landraces, sarta ditampilkeun pungency rada luhur. Sanajan kitu, rasa amis dina bawang téh alatan kasaimbangan antara kandungan gula jeung rasa haseum, ku kituna karakterisasi ieu bisa jadi mangpaat pikeun ngarojong seleksi genotip tina nilai, biasana dilaksanakeun ku patani ngan dumasar kana morfologi.
spidol SSR dikonfirmasi janten alat mangpaat pikeun ngabedakeun genotypes, sanajan dikumpulkeun dina wewengkon tumuwuh sempit kayaning kota Acquaviva delle Fonti. Pananda anu dipilih nunjukkeun jumlah alél anu langkung luhur tibatan spidol anu dilaporkeun saméméhna ku [43] jeung [44], tapi leuwih handap tina spidol dilaporkeun ku [45]. Sumawona, 50% tina set spidol urang nunjukkeun nilai indéks PIC langkung ageung tibatan 0.5, ngabuktikeun cocog pikeun ngabentenkeun populasi dina koleksi, sakumaha anu disarankeun ku [46]. Assessment of diversity dina populasi ngungkabkeun nilai sarupa antara Ho jeung He, hasilna Fi lows nilai-nilai. Ieu sapuk jeung alam kaluar-nyebrang tina A. cepa, nu serius nalangsara ti depresi inbreeding [47]. The sakabéh Fis nilai diitung dina populasi bawang dianggap dina ulikan ieu (0.054) leuwih handap ti nu saméméhna dilaporkeun ku [45] (0.22) sarta ampir sarua jeung nu kapanggih ku [31] (0.08) jeung [48] (0.00) anu ditaksir diversity genetik dina landraces bawang ti kalér-kuloneun Spanyol sarta Niger, mungguh. Tingkat heterozigositas anu penting dina populasi ARO nguatkeun anggapan yén Apulia ngagambarkeun pusat karagaman pikeun seueur spésiés hortikultura. [32, 42, 49-hiji].
AMOVA nyorot yén kalolobaan variasi molekular dina kumpulan genotyped dina ulikan ieu aya dina populasi. Sanajan kitu, diferensiasi genetik signifikan diantara populasi (FPT nilai) nembongkeun lumangsungna stratifikasi genetik. Kanyataanna, sanajan hasil kami nunjukkeun ayana uniformity genetik dina kalolobaan populasi ARO, ngabentuk klaster well-diartikeun, populasi ARO7 na ARO12 ditampilkeun profil genetik jelas béda. Hasil ieu bisa jadi alatan asal béda tina siki dipaké ku dua patani ti mana populasi dikumpulkeun. Sumawona, dumasar kana hasil anu dicandak, landrace ARO tiasa dianggap jelas béda dina tingkat genetik ti landraces TRO sareng MCO. Dina ulikan panganyarna, [29] ditaksir karagaman genetik sababaraha landraces bawang Italia kaasup "Acquaviva," "Tropea," jeung "Montoro". Sanajan pangarang ngagunakeun spidol SNP pikeun meunteun karagaman genetik koleksi bawang bombay anu leuwih lega, genotyping henteu tiasa ngabedakeun "Acquaviva" tina bawang "Tropea" sareng "Montoro". Panginten, bédana ieu disababkeun ku nilai PIC rata-rata anu rendah (0.292), nunjukkeun inpormasi umum anu sederhana tina loci anu dianalisis sakumaha anu diklaim ku [29]. Saterusna, dina raraga nalungtik ayana sub-struktur dina klaster Italia maranéhanana, éta bakal geus hadé pikeun nganalisis genotypes Italia misah ti sesa koleksi. Panginten éta bakal tiasa ngabayangkeun pola karagaman genetik anu aya hubunganana sareng stratifikasi géografis atanapi sipat-sipat dina pilihan émpiris.
Kacindekan, ulikan ieu ngagambarkeun laporan komprehensif ngeunaan landrace bawang pakait sareng warisan budaya lokal sarta pentingna ékonomi pikeun patani. Hasil kami nyorot yén, sareng sababaraha pengecualian, ARO dicirikeun ku kolam renang gén anu jelas, anu pantes dilestarikan tina résiko erosi genetik. Ku alatan éta, ngadegna kumpulan wawakil sumber berharga ieu diversity genetik geus krusial. Tungtungna, karakterisasi genetik sareng fenotip ARO tiasa mangpaat pikeun kéngingkeun tanda kualitas ti Uni Éropa.
Bahan jeung Métode
Koléksi Plasma Nutfah, Bahan Tutuwuhan, sareng Ekstraksi DNA
Sakumpulan 13 populasi ARO landrace dicandak dina kerangka proyék Apulia Region (BiodiverSO: https://www.biodiversitapuglia.it/), ngaliwatan runtuyan misi dilumangsungkeun dina "Acquaviva delle Fonti", hiji kota leutik Apulian di Propinsi Bari, Italia. Situs kumpulan unggal aksés dipetakeun ngaliwatan Sistem Émbaran Geografis (GIS) sareng dilaporkeun dina Tabel 4. Sajaba ti éta, dua populasi ti landrace TRO jeung hiji populasi ti landrace MCO anu kaasup dina ulikan ayeuna sarta dipaké salaku rujukan. Kabéh bahan tutuwuhan ieu dipelak dina kaayaan lingkungan anu sarua di tegalan eksperimen "P Martucci" Universitas Bari (41 ° 1'22.08″ N, 16 ° 54'25.95″ E), dina kandang panyalindungan pikeun nyegah penyerbukan silang diantara. populasi jeung assuring pembuahan intra-populasi ku cara blowflies (Lucilia Caesar). Populasi 16 dicirian pikeun sipat anu aya hubunganana sareng ukuran sareng bentuk bohlam sareng warna kulit sareng daging (Tabel S1). Sajaba ti éta, assay eusi larut padet dipigawé maké refractometer leungeun-diayakeun sarta pungency diukur dina sampel jus bawang nambahkeun 2,4-dinitrophenyl hydrazine (0.125%). v/v dina 2N of HCl) jeung evaluating absorbance dina 420 nm, sakumaha dilaporkeun ku [31]. Uji rentang ganda Duncan jeung uji SNK dilaksanakeun pikeun nangtukeun ayana béda anu signifikan.
Méja 4. Daptar Populasi Dikumpulkeun jeung Genotyped dina Panalungtikan ieu. Pikeun Unggal Populasi, Kode Idéntifikasi, Ngaran Lokal, Koordinat GPS, sareng Bank Gene Ngawétkeun Sikina Dilaporkeun.
| Code | nami | GPS Koordinat | Bank Gene y |
| ARO1 | Cipolla rossa di Acquaviva | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO2 | Cipolla rossa di Acquaviva | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO3 | Cipolla rossa di Acquaviva | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO4 | Cipolla rossa di Acquaviva | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO5 | Cipolla rossa di Acquaviva | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO6 | Cipolla rossa di Acquaviva | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO7 | Cipolla rossa di Acquaviva | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO8 | Cipolla rossa di Acquaviva | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO9 | Cipolla rossa di Acquaviva | 40°54'51.372″ N 16°49'3.504" E | Di.SSPA |
| ARO10 | Cipolla rossa di Acquaviva | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO11 | Cipolla rossa di Acquaviva | 40°52'49.8″ N 16°49'48.575" E | Di.SSPA |
| ARO12 | Cipolla rossa di Acquaviva | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO13 | Cipolla rossa di Acquaviva | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa lunga di Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | Cipolla ramata di Montoro | - | Di.SSPA |
| y Di.SSPA, Jurusan Taneuh, Tutuwuhan jeung Élmu Pangan, Universitas Bari. |
Bahan daun tina 20 genotipe per populasi disampel sareng disimpen dina suhu -80 °C dugi ka dianggo. Pikeun spésiés beunghar polisakarida, salaku A. cepa, léngkah munggaran miceun polisakarida penting pikeun ménta DNA kualitas alus, kituna washes awal dina panyangga STE (0.25 M sukrosa, 0.03 M Tris, 0.05 M EDTA) dipigawé sakumaha ditétélakeun ku [52]. Total DNA diekstrak nuturkeun metode CTAB [53] sarta pamustunganana éta dipariksa pikeun kualitas sarta konsentrasi ku Nano Drop 2000 UV-vis spéktrofotométer (ThermoScientific, Waltham, MA, AS) jeung 0.8% agarose gél éléktroforésis.
Analisis SSR
16 kombinasi primer EST-SSR dikembangkeun ku [54] sarta saméméhna diuji dina studi diversity genetik ku [43] jeung [44] jeung 21 SSR génomik [45-hiji] disaring pikeun meunteun kasesuaianna (Tabel Tambahan S4). Genotyping dilakukeun nganggo metode tag fluoresensi ékonomi dimana buntut M13 ditambahkeun kana unggal primer SSR maju. [56]. Campuran PCR disiapkeun dina réaksi 20 gL anu ngandung: 50 ng total DNA, 0.2 mM campuran dNTP, 1X panyangga réaksi PCR, 0.8 U tina DreamTaq DNA polimérase (Thermo Scientific, Waltham, MA, USA), 0.16 gM tina reverse primer , 0.032 gM of primer maju dilegaan ku runtuyan M13 (5′-TGTAAAACGACGGCCAGT-3 ′), jeung 0.08 gM of a primer M13 universal dilabélan ku FAM atanapi NED dyes fluoresensi (Sigma-Aldrich, St. Louis, MO, AS). Réaksi PCR dilaksanakeun dina thermocycler SimpliAmp (Applied Biosystems, CA, USA) kalayan kaayaan di handap ieu pikeun mayoritas pasangan primer: 94 °C salila 5 mnt, 40 siklus dina 94 °C salila 30 detik, 58 °C. salila 45 s jeung 72 ° C salila 45 s sarta elongation final dina 72 ° C salila 5 mnt. Sedengkeun pikeun ACM446 sareng ACM449, PCR touchdown diterapkeun kalayan annealing 60 ° C dugi ka 55 ° C dina 10 siklus, 30 siklus dina 55 ° C, dituturkeun ku perpanjangan akhir 5 mnt dina 72 ° C. Produk PCR dimuat kana piring 96-sumur sareng dicampur sareng 14 gL Hi-Di Formamide (Life Technologies, Carlsbad, CA, AS) sareng 0.5 gL GeneScan 500 ROX Size Standard (Life Technologies, Carlsbad, CA, USA). Amplicons direngsekeun ku cara ABI PRISM 3100 Avant Genetic Analyzer (Life Technologies, Carlsbad, CA, USA) mesin sequencing kapiler, dimana alél anu ngoleksi salaku co-dominan jeung ditugaskeun ku ngagunakeun GeneMapper Software Vérsi 3.7.
Parangkat lunak GenAlEx 6.5 [57] sarta Cervus 3.0.7 [58] digunakeun pikeun ngira-ngira jumlah alél (Na), jumlah alél éféktif (Ne), heterozigositas observasi (Ho), heterozigositas ekspektasi (He), eusi informasi polimorfik (PIC), indéks informasi Shannon (I), jeung indéks fiksasi (Fis). ) pikeun tiap lokus SSR.
Penilaian Keragaman Genetik
Pembagian hirarki variasi genetik diantara sareng dina populasi bawang dievaluasi ku GenAlEx 6.5 [57] ngaliwatan analisis varian molekular (AMOVA) kalawan 999 bootstrapping pikeun nguji signifikansi. Leuwih ti éta, software GenAlEx 6.5 dipaké pikeun ngira-ngira karagaman dina unggal populasi ku cara ngitung rata-rata Ho, He, jeung Fis dina sakabéh loci SSR.
Struktur populasi disimpulkeun ku algoritma clustering basis model Bayesian dilaksanakeun dina software STRUCTURE v.2.3.4. [59]. Susunan data dijalankeun kalawan sababaraha klaster hipotétis (K), mimitian ti 1 nepi ka 10, netepkeun sapuluh lumpat mandiri per unggal nilai K. Pikeun unggal ngajalankeun, dimaksudkeun pikeun pariksa konsistensi hasil, 100,000 mimiti kaduruk-di jaman jeung 100,000 Markov Chain Monte Carlo (MCMC) iterations dipigawé dina modél admixture sarta frékuénsi alél bebas diantara populasi. Nilai K paling dipikaresep ditangtukeun ngalaksanakeun métode AK, digambarkeun ku [60], dina program basis web STRUCTURE HARVESTER [61]. Populasi individu ditugaskeun ka klaster husus nalika koefisien kaanggotaan na (q-nilai) leuwih luhur ti 0.7, disebutkeun eta dianggap katurunan admixed.
Analisis koordinat poko dilakukeun pikeun ngabayangkeun pola hubungan genetik diantara aksés anu diungkabkeun ku matriks jarak genetik Nei (Tabel Tambahan S5). Dumasar kana frékuénsi alél, dendrogram jarak genetik diwangun ngagunakeun métode grup pasangan unweighted kalawan rata-rata arithmetic (UPGMA) analisis klaster dina software POPTREEW. [62]. Bootstrapping diterapkeun pikeun meunteun kapercayaan dina klaster hirarkis, netepkeun 100 resampling set data. Tungtungna, software MEGA X [63] ieu dipaké salaku software gambar tangkal.
Bahan tambahan: Ieu atos sayogi online di http://www.mdpi.com/2223-7747/9/2/260/s1. Tabél S1: Karakterisasi morfologis bohlam ARO, MCO, jeung TRO. Tabél S2: Heterozygosity sarta indéks fiksasi diitung keur landraces ARO jeung landraces TRO na MCO. Tabél S3: Nilai pasangan tina parameter Fpt. Tabél S4: Daptar SSR anu digunakeun dina pangajaran. Tabél S5. Matriks populasi pasangan tina jarak genetik Nei. Gambar S1: Bagan garis nilai K robah ku Evanno Delta K.
Panulis kontribusi: CL jeung LR conceived ulikan sarta dirancang percobaan; CL jeung PI dipigawé analisis spidol molekular; ARM sareng VZ ngalaksanakeun uji lapangan; RM, SP, GR, jeung CL aub dina analisis data; RM jeung CL nulis naskah. Sadaya pangarang parantos maca sareng satuju kana versi naskah anu diterbitkeun.
waragad: Karya ieu dibiayaan ku proyék Regional Apulian "Keanekaragaman hayati spésiés sayur Apulian" -Programma di Sviluppo Rurale per la Puglia 2014-2020. Misura 10—Sottomisura 10.2; hibah CUP H92C15000270002, Italia.
Acknowledgments: Acknowledgments alatan "Azienda Agricola Iannone Anna" jeung "Associazione produttori della vera cipolla rossa di Acquaviva" pikeun nyadiakeun bahan tutuwuhan dipaké dina percobaan.
Bentrok of Minat: Nu nulis dibewarakeun aya konflik of interest.
Rujukan
- 1. Stearn, WT Sabaraha spésiés Allium anu dipikanyaho? Kew Mag. 1992, 9, 180-182. [CrossRef]
- 2. FAOSTAT. Database Statistik FAO. Sadia online: http://www.fao.org/2017 (diaksés tanggal 8 Januari 2019).
- 3. Blok, E. Kimia bawang bodas jeung bawang. Sci. Am. 1985, 252, 114-119. [CrossRef]
- 4. Lee, B.; Jung, JH; Kim, HS Assessment tina bawang beureum dina aktivitas antioksidan dina beurit. Kimia Dahareun. Toksikol. 2012, 50, 3912-3919. [CrossRef]
- 5. Lee, SM; Bulan, J.; Chung, JH; Cha, YJ; Shin, MJ Pangaruh ekstrak kulit bawang anu beunghar ku quercetin dina trombosis arteri dina beurit. Kimia Dahareun. Toksikol. 2013, 57, 99-105. [CrossRef] [PubMed]
- 6. Yoshinari, O.; Shiojima, Y.; Igarashi, K. épék anti obesitas ekstrak bawang di zucker beurit lemak diabetik. gizi 2012, 4,1518-1526. [CrossRef]
- 7. Akash, MSH; Rahman, K.; Chen, S. Spice plant Allium cepa: Suplemén dietary pikeun pengobatan diabetes mellitus tipe 2. jat nu mawa gisi 2014, 30, 1128-1137. [CrossRef] [PubMed]
- 8. Wang, Y.; Tian, WX; Ma, XF Inhibitory Balukar tina bawang (Allium cepa L.) ékstrak on proliferasi sél kanker sarta adiposit via inhibiting asam lemak sintase. Asian Pac. J. Kangker Prev. 2012,13, 5573-5579. [CrossRef] [PubMed]
- 9. Lai, WW; Hsu, SC; Ceuh, FS; Chen, YY; Yang, JS; Lin, JP; Lien, JC; Tsai, CH; Chung, JG Quercetin nyegah migrasi sarta invasi sél kanker lisan manusa SAS ngaliwatan inhibisi NF-kappaB jeung matrix metalloproteinase-2/-9 jalur signalling. Antikanker Res. 2013, 33, 1941-1950. [PubMed]
- 10. Nicastro, HL; Ross, SA; Milner, JA Bawang bodas jeung bawang: sipat pencegahan kanker maranéhanana. Kanker Prev. Res. 2015, 8,181-189. [CrossRef]
- 11. Forte, L.; Torricelli, P.; Boanini, E.; Gazzano, M.; Rubini, K.; Fini, M.; Bigi, A. Antioksidan jeung perbaikan tulang sipat quercetin-functionalized hydroxyapatite: Hiji studi ko-budaya sél osteoblast-osteoclast-endothelial in vitro. Acta Biomatér. 2016, 32, 298-308. [CrossRef]
- 12. Yamazaki, Y.; Iwasaki, K.; Mikami, M.; Yagihashi, A. Distribusi sabelas prékursor rasa, turunan S-Alk(en)yl-L-sistein, dina tujuh sayuran Allium. Pangan Sci. Téknologi. Res. 2011, 17, 55-62. [CrossRef]
- 13. Blok, E. Kimia organosulfur tina Genus Allium-Implikasi pikeun kimia organik walirang. Angew. Kimia. Int. Ed. Engl. 1992, 31, 1135-1178. [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; Thomas, B.; Smith, B. Bawang-A benefit global pikeun kaséhatan. Phytother. Res. 2002,16, 603-615. [CrossRef]
- 15. Schwimmer, S.; Weston, WJ Pangwangunan énzimatik asam piruvat dina bawang bombay salaku ukuran pungency. J. Agric. Kimia Dahareun. 1961, 9, 301-304. [CrossRef]
- 16. Ketter, CAT; Randle, WM Pungency assessment dina bawang. Di Studi Diuji pikeun Pangajaran Laboratorium; Karcher, SJ, Ed.; Asosiasi pikeun Atikan Laboratorium Biologi (BISA): New York, NY, AS, 1998; Jilid 19, kaca 177-196.
- 17. Hanelt, P Taksonomi, évolusi, jeung sajarah. Di Bawang sareng Pepelakan Sekutu, Vol. I. Botani, Fisiologi jeung Géologi; Rabinowitch, HD, Brewster, JL, Eds.; CRC Pencét: Boca Raton, FL, AS, 1990; kaca 1-26.
- 18. Rabinowitch, HD; Curah, L. Élmu Pamotongan Allium: Kamajuan Anyar; Publishing CABI: Wallingford, UK, 2002.
- 19. Mallor, C.; Carravedo, M.; Éstopanan, G.; Mallor, F. Karakterisasi sumberdaya genetik bawang (Allium cepa L.) ti puseur sekundér Spanyol of diversity. bentang. J. Agric. Res. 2011, 9, 144-155. [CrossRef]
- 20. Ferioli, F.; D'Antuono, LF Evaluasi phenolics jeung sistein sulfoxides dina bawang lokal jeung germplasm shallot ti Italia jeung Ukraina. Genet. Résour. Pamotongan Evol. 2016, 63, 601-614. [CrossRef]
- 21. Petropoulos, SA; Fernandes, A.; Barros, L.; Ferreira, ICFR; Ntatsi, G. Pedaran morfologis, gizi jeung kimia 'vatikiotiko', hiji landrace lokal bawang ti Yunani. Kimia Dahareun. 2015,182, 156-163. [CrossRef]
- 22. Liguori, L.; Adiletta, G.; Nazzaro, F.; Fratianni, F.; Di Matteo, M.; Albanese, D. Biokimia, sipat antioksidan sarta aktivitas antimikrobial variétas bawang béda di wewengkon Tengah. J. Pangan Meas. karakter. 2019,13, 1232-1241. [CrossRef]
- 23. Yoo, KS; Pike, L.; Crosby, K.; Jones, Urang Sunda; Leskovar, D. Bedana dina pungency bawang alatan kultivar, lingkungan tumuwuh, sarta ukuran bohlam. Sci. Hortik. 2006,110, 144-149. [CrossRef]
- 24. Beesk, N.; Perner, H.; Schwarz, D.; George, E.; Kroh, LW; Rohn, S. Distribusi quercetin-3, 4′-O-diglucoside, quercetin-4′-O-monoglucoside, sarta quercetin dina bagian nu sejen bohlam bawang (Allium cepa L.) dipangaruhan ku genotype. Kimia Dahareun. 2010,122, 566-571. [CrossRef]
- 25. Caruso, G.; Conti, S.; Villari, G.; Borrelli, C.; Melchionna, G.; Minutolo, M.; Russo, G.; Amalfitano, C. Balukar waktos transplanting sareng dénsitas tutuwuhan dina ngahasilkeun, kualitas sareng kandungan antioksidan bawang bombay. (Allium cepa L.) di Italia kidul. Sci. Hortik. 2014,166, 111-120. [CrossRef]
- 26. Perez-Gregorio, Bapak; Regueiro, J.; Simal-Gandara, J.; Rodrigues, AS; Almeida, DPF Ngaronjatkeun nilai tambah tina bawang salaku sumber flavonoid antioksidan: Tinjauan kritis. Crit. Pdt Sci. Nutr. 2014, 54,1050-1062. [CrossRef] [PubMed]
- 27. Pohnl, T.; Schweiggert, RM; Carle, R. Dampak metode budidaya sareng pilihan kultivar kana karbohidrat larut sareng prinsip pedas dina bawang. (Allium cepa L.). J. Agric. Kimia Dahareun. 2018, 66, 12827-12835. [CrossRef] [PubMed]
- 28. Tedesco, I.; Karbon, V.; Spagnuolo, C.; Minasi, P.; Russo, GL Idéntifikasi sareng kuantifikasi flavonoid tina dua kultivar Italia kidul allium cepa L., Tropea (bawang beureum) jeung Montoro (bawang tambaga), sarta kapasitas maranéhna pikeun ngajaga éritrosit manusa tina setrés oksidatif. J. Agric. Kimia Dahareun. 2015, 63, 5229-5238. [CrossRef]
- 29. Villano, C.; Esposito, S.; Carucci, F.; Frusciante, L.; Carputo, D.; Aversano, R. High-throughput genotyping dina bawang nembongkeun struktur diversity genetik na SNPs informatif mangpaat pikeun beternak molekular. Mol. Katurunan. 2019, 39, 5. [CrossRef]
- 30. Mercati, F.; Longo, C.; Poma, D.; Araniti, F.; Lupini, A.; Mammano, MM; Fiore, MC; Abenavoli, MR; Sunseri, F. Variasi genetik tina tomat umur rak panjang Italia (Solanum lycopersicum L.) ngumpulkeun ku ngagunakeun SSR jeung morfologis tret buah. Genet. Résour. Pamotongan Evol. 2014, 62, 721-732. [CrossRef]
- 31. Gonzalez-Perez, S.; Mallor, C.; Garces-Claver, A.; Merino, F.; Taboada, A.; Rivera, A.; Pomar, F.; Perovic, D.; Silvar, C. Ngalanglang diversity genetik na Tret kualitas dina kumpulan bawang (Allium cepa L.) landraces ti kalér-kuloneun Spanyol. Genetika 2015, 47, 885-900. [CrossRef]
- 32. Lotti, C.; Iovieno, P.; Centomani, I.; Marcotrigiano, AR; Fanelli, V.; Mimiola, G.; Summo, C.; Pawan, S.; Ricciardi, L. Genetik, bio-agronomik, sareng karakterisasi gizi kale (brassica oleracea L. var. acephala) diversity di Apulia, Italia Kidul. diversity 2018,10, 25. [CrossRef]
- 33. Bardaro, N.; Marcotrigiano, AR; Bracuto, V.; Mazzeo, Urang Sunda; Ricciardi, F.; Lotti, C.; Pawan, S.; Ricciardi, L. analisis genetik lalawanan ka Orobanche crenata (Forsk.) dina kacang polong (Pisum sativum L.) garis strigolactone low. J. Tutuwuhan Pathol. 2016, 98, 671-675.
- 34. Wako, T.; Tsukazaki, H.; Yaguchi, S.; Yamashita, K.; Ito, S.; Shigyo, M. Mapping of loci tret kuantitatif pikeun bolting waktos di bunching bawang (Allium fistulosum L.). Euphytica 2016, 209, 537-546. [CrossRef]
- 35. Dhaka, N.; Mukhopadhyay, A.; Paritosh, K.; Gupta, V.; Pental, D.; Pradhan, AK Identification of SSRs gén jeung pangwangunan peta linkage basis SSR di Brassica juncea. Euphytica 2017, 213, 15. [CrossRef]
- 36. Anandhan, S.; Mote, SR; Gopal, J. Evaluasi identitas varietal bawang maké spidol SSR. Biji Sci. Téknologi. 2014, 42, 279-285. [CrossRef]
- 37. Mitrova, K.; Svoboda, P.; Ovesna, J. Pamilihan sareng validasi set spidol pikeun diferensiasi kultivar bawang tina Céko. Czech J. Genet. Tutuwuhan Breed. 2015, 51, 62-67. [CrossRef]
- 38. Di Rienzo, V.; Miazzi, MM; Fanelli, V.; Sabetta, W.; Montemurro, C. The pelestarian sarta characterization of Apulian zaitun germplasm biodiversity. Acta Hortic. 2018,1199,1-6. [CrossRef]
- 39. Mallor, C.; Arnedo-Andres, A.; Garces-Claver, A. Assessing diversity genetik Spanyol allium cepa landraces pikeun beternak bawang maké spidol microsatelit. Sci. Hortik. 2014,170, 24-31. [CrossRef]
- 40. Rivera, A.; Mallor, C.; Garces-Claver, A.; Garcia-Ulloa, A.; Pomar, F.; Silvar, C. Assessing karagaman genetik dina bawang (allium cepa L.) landraces ti kalér-kuloneun Spanyol sarta ngabandingkeun jeung variability Éropa. NZJ Crop Hortic. 2016, 44, 103-120. [CrossRef]
- 41. De Giovanni, C.; Pawan, S.; Taranto, F.; Di Rienzo, V.; Miazzi, MM; Marcotrigiano, AR; Mangini, G.; Montemurro, C.; Ricciardi, L.; Lotti, C. variasi genetik tina kumpulan germplasm global chickpea (Cicer arietinum L.) kaasup accessions Italia dina resiko erosi genetik. Fisiol. Mol. Biol. Tatangkalan 2017, 23, 197-205. [CrossRef]
- 42. Mazzeo, Urang Sunda; Morgese, A.; Sonnante, G.; Zuluaga, DL; Pawan, S.; Ricciardi, L.; Lotti, C. diversity genetik dina brokoli rabe (Brassica rapa L. subsp. sylvestris (L.) Janch.) ti Italia Kidul. Sci. Hortik. 2019, 253, 140-146. [CrossRef]
- 43. Jakse, M.; Martin, W.; McCallum, J.; Havey, M. polymorphisms nukléotida tunggal, indels, sarta runtuyan basajan repeats pikeun idéntifikasi cultivar bawang. J. Am. Soc. Hortik. Sci. 2005,130, 912-917. [CrossRef]
- 44. McCallum, J.; Thomson, S.; Pither-Joyce, M.; Kenel, F. analisis diversity genetik na single-nukléotida polymorphism ngembangkeun spidol dina bawang bohlam dibudidayakan dumasar kana runtuyan dikedalkeun tag-basajan runtuyan spidol ulang. J. Am. Soc. Hortik. Sci. 2008,133, 810-818. [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; Wright, K.; Chen, L.; McCallum, J. Ngembangkeun spidol ulang runtuyan basajan génomik mantap pikeun estimasi diversity genetik dina na diantara bohlam bawang. (Allium cepa L.) populasi. Mol. Katurunan. 2012, 30, 1401-1411. [CrossRef]
- 46. DeWoody, JA; Honeycutt, RL; Skow, LC Microsatelit spidol dina kijang buntut bodas. J. Hered. 1995, 86, 317-319. [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D. bawang Iran (Allium cepa L.) kultivar réspon kana depresi inbreeding. Dunya Appl. Sci. J. 2010,11, 426-428.
- 48. Abdou, R.; Bakasso, Y.; Saadou, M.; Baudoin, JP; Hardy, OJ Keragaman genetik bawang Niger (Allium cepa L.) ditaksir ku spidol ulang runtuyan basajan (SSR). Acta Hortic. 2016,1143, 77-90. [CrossRef]
- 49. Pawan, S.; Lotti, C.; Marcotrigiano, AR; Mazzeo, Urang Sunda; Bardaro, N.; Bracuto, V.; Ricciardi, F.; Taranto, F.; D'Agostino, N.; Schiavulli, A.; jeung sajabana. Kluster genetik anu béda dina buncis anu dibudidayakeun sakumaha anu diungkabkeun ku panemuan pananda génom sareng genotyping. Génom tutuwuhan 2017, 2017,10. [CrossRef]
- 50. Pawan, S.; Marcotrigiano, AR; Ciani, E.; Mazzeo, Urang Sunda; Zonno, V.; Ruggieri, V.; Lotti, C.; Ricciardi, L. Genotyping-demi-sequencing of melon a (Cucumis melo L.) kumpulan germplasm ti puseur sekundér diversity highlights pola variasi genetik na fitur génomik of pools gén béda. BMC Génom. 2017, 18, 59. [CrossRef]
- 51. Di Rienzo, V.; Sion, S.; Taranto, F.; D'Agostino, N.; Montemurro, C.; Fanelli, V.; Sabetta, W.; Boucheffa, S.; Tamendjari, A.; Pasqualone, A.; jeung sajabana. Aliran genetik diantara populasi zaitun dina baskom Tengah. Peer J. 2018, 6. [CrossRef]
- 52. Angon, LD; McLay, TG Dua protokol skala mikro pikeun isolasi DNA tina jaringan tutuwuhan beunghar polisakarida. J. tutuwuhan Res. 2011,124, 311-314. [CrossRef]
- 53. Doyle, JJ; Doyle, JL Isolasi DNA tutuwuhan tina jaringan seger. Focus 1990,12, 13-14.
- 54. Kuhl, JC; Cheung, F.; Qiaoping, Y.; Martin, W.; Zewdie, Y.; McCallum, J.; Catanach, A.; Rutherford, P.; Tilelep, KC; Jenderek, M.; jeung sajabana. Hiji set unik tina 11,008 tag runtuyan dikedalkeun bawang nembongkeun runtuyan dikedalkeun sarta béda génomik antara pesenan monocot asparagales na poales. Sél Tutuwuhan 2004,16, 114-125. [CrossRef]
- 55. Kim, HJ; Lee, HR; Hyun, JY; Lagu, KH; Kim, KH; Kim, JE; Hur, CG; Harn, CH Marker ngembangkeun pikeun nguji purity genetik bawang maké SSR Panimu. Koréa J. Breed. Sci. 2012, 44, 421-432. [CrossRef]
- 56. Schuelke, M. Hiji métode ékonomi pikeun panyiri fluoresensi tina fragmen PCR. Nat. Biotéhnologi. 2000, 18, 233-234. [CrossRef] [PubMed]
- 57. Peakall, Urang Sunda; Smouse, PE GenAlEx 6.5: Analisis genetik dina Excel. Parangkat lunak genetik populasi pikeun pangajaran sareng panalungtikan: Pembaruan. Bioinformatika 2012, 28, 2537-2539. [CrossRef] [PubMed]
- 58. Kalinowski, ST; Taper, ML; Marshall, TC Revising kumaha program komputer CERVUS accommodates kasalahan genotyping naek kasuksésan dina ngerjakeun kabapakan. Mol. Ékol. 2007,16, 1099-1106. [CrossRef]
- 59. Pritchard, JK; Stephens, M.; Rosenberg, NA; Donnelly, P. Asosiasi pemetaan dina populasi terstruktur. Am. J. Hum. Genet. 2000, 67, 170-181. [CrossRef]
- 60. Evanno, G.; Regnaut, S.; Goudet, J. Ngadeteksi jumlah klaster individu ngagunakeun STRUKTUR software: Hiji studi simulasi. Mol. Ékol. 2005,14, 2611-2620. [CrossRef]
- 61. Earl, D.; VonHoldt, B. STRUKTUR HARVESTER: A ramatloka jeung program pikeun visualizing kaluaran STRUKTUR sarta ngalaksanakeun métode Evanno. Konservasi. Genet. Résour. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW: Vérsi wéb POPTREE pikeun ngawangun tangkal populasi tina data frékuénsi alél sareng ngitung sababaraha kuantitas anu sanés. Mol. Biol. Evol. 2014, 31, 1622-1624. [CrossRef]
- 63. Kumar, S.; Stecher, G.; Li, M.; Knyaz, C.; Tamura, K. MEGA X. Molekul Évolusionér Genetika Analisis sakuliah platform komputasi. Mol. Biol. Evol. 2018, 35, 1547-1549. [CrossRef]